新着情報
サギソウの病原ウイルスHaMVのゲノム配列を明らかにしました。
[著者] Kondo, H., Maeda, T., Gara, I.W., Chiba, S., Maruyama, K., Tamada, T. and Suzuki, N.
[論文タイトル] Complete genome sequence of Habenaria mosaic virus, a new potyvirus species infecting a terrestrial orchid (Habenaria radiata) in Japan
[掲載論文] Archives of Virology 159, 163-166 (2014)
[共同研究] 日本大学との共同研究
[使用した共通機器] 透過型電子顕微鏡、超遠心分離機、DNAシークエンサー
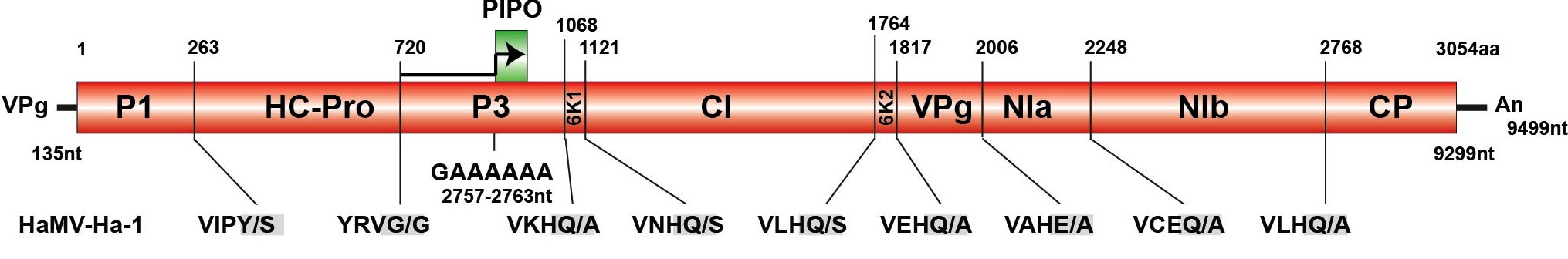
[内容紹介] サギソウ(鷺草, Habenaria radiata)は湿地に生息する多年性のラン科植物で、花の唇弁がシラサギの様子に似ていることからご存じな方も多いと思います。しかし、乱獲や自生地である湿地の消滅や環境変化で個体数は減少しており、準絶滅危惧種に指定されています。現在、サギソウをはじめ野生ランの自生地の復元・保護活動(「植え戻し」と呼ばれる)が各地で行われていますが、これは人為的に増殖したランを植え戻すというものです。しかし、その増殖過程でウイルスに罹病する場合があり、もし気がつかないまま植え戻してしまうと自生地にウイルスを持ち込んでしまう危険性が指摘されています。これまで、サギソウの病原ウイルスとしては、サギソウモザイクウイルス(Habenaria mosaic virus, HaMV)とスイカモザイクウイルス(Watermelon mosaic virus, WMV)が知られていました。両者はポティウイルス属(Potyvirus)のメンバーと考えられますが、HaMVについてはゲノム情報が未解明のままでした。本研究では、このHaMVのゲノムRNAが9,499塩基からなり、3,054アミノ酸残基のポリ蛋白質をコードすることを明らかにしました。さらに、既知のポティウイルスとの配列相同性から、HaMVが新規のポティウイルス種であると結論しました。本研究の成果を踏まえ、サギソウのポティウイルスについて遺伝子診断体制を整備することにより、ウイルスをサギソウ自生地に蔓延させてしまうリスクを低減できると考えられます。(文責:近藤秀樹)
お問い合わせ先: 植物・微生物相互作用グループ