
研究組織
統合ゲノム育種グループ
| 統合ゲノム育種グループのホームページへ |
教員
 |
教授: 山本 敏央 Prof. Dr. Toshio Yamamoto E-mail: yamamo101040@(@以下はokayama-u.ac.jp を付けてください。) 専門分野: 作物育種学 |
||
 |
准教授: 長岐 清孝 Associate Prof. Dr. Kiyotaka Nagaki E-mail: nagaki@(@以下はokayama-u.ac.jp を付けてください。) 専門分野: 分子細胞遺伝解析学 |
||
 |
准教授: 古田 智敬 Associate Prof. Dr. Tomoyuki Furuta E-mail: f.tomoyuki@(@以下はokayama-u.ac.jp を付けてください。) 専門分野: 植物遺伝育種学 |
主な研究テーマ
| 1. 多様なイネ遺伝資源が持つ有用農業形質の探索と活用 イネの生産性や環境ストレス耐性を素材として、品種改良の原動力である国内外の多様なイネ遺伝資源の特徴をゲノム構成の観点から明らかにし、さまざまな育種目標に対応可能な遺伝子(群)を見出す方法を検討します。また交雑育種におけるゲノムや染色体の動態を明らかにし、有用な遺伝子や農業形質を最短で栽培品種に取り込むような新しい育種技術を検証します。 |
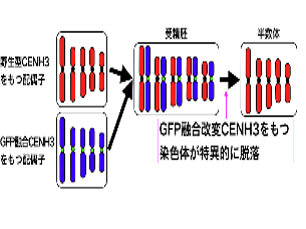
| 2. 動原体改変による半数体の作出 半数体は倍加半数体による育種年限の短期化に利用できますが、半数体が得られる種は限られています。シロイヌナズナやトウモロコシでは、動原体の機能を部分的に失わせた系統と野生型系統を交配すると野生型系統由来の染色体をもつ半数体ができることが報告されました。私たちはこれまでの基礎研究で得られた結果を活かし、これらの種で用いられた方法を簡便化することにより多くの種で利用可能な半数体作出系を開発しています。 |
 |
| 3. バイオインフォマティクスと統計遺伝学に基づく高効率迅速育種法の開発 大規模な環境変動や急激な人口増加に対応するために、迅速で効率的な作物育種法の開発がますます必要とされています。しかし従来の育種法では、複数回に渡る交配と形質調査を繰り返すため、どうしても時間がかかってしまいます。そこで、これまで蓄積されてきた遺伝学や生理学、作物学などにおける様々なデータとゲノム情報をフル活用し、育種プロセスを短縮する新たな手法の開発を目指しています。 |
Latest publications (for complete and most current publications visit group pages)
(1) Tsukahara S, Bousios A, Kreszies T, Perez-Roman E, Yamaguchi S, Leduque B, Nakano A, Naish M, Osakabe A, Toyoda A, Ito H, Edera A, Tominaga S, Juliarni, Kato K, Oda S, Inagaki S, Lorković Z, Nagaki K, Berger F, Kawabe A, Quadrana L, Henderson I, Kakutani T. Centrophilic retrotransposon integration via CENH3 chromatin in Arabidopsis. Nature. 637: 744-748. doi.org/10.1038/s41586-024-08319-7 (2025. 1.)
(2) Akagi T, Fujita N, Shirasawa K, Tanaka H, Nagaki K, Masuda K, Horiuchi A, Kuwada E, Kawai K, Kunou R, Nakamura K, Ikeda Y, Toyoda A, Itoh T, Ushijima K, Charlesworth D. Rapid and dynamic evolution of a giant Y chromosome in Silene latifolia. Science. 387: 637-643. doi.org/10.1126/science.adk9074 (2025. 2.)
(3) Nagaki K, Narusaka M, Narusaka Y. Elucidation of the phylogenetic relationships among Alpinia species native to the Nansei Islands, Japan. Cytologia. 90: 29-36. doi.org/10.1508/cytologia.90.29 (2025. 3.)
(4) Nagaki K, Ushijima K, Akagi T, Tanaka K, Kobayashi H. Pancentromere analysis of Allium species reveals diverse centromere positions in onion and gigantic centromeres in garlic. Plant Cell. 37: koaf142. doi.org/10.1093/plcell/koaf142 (2025. 6.)
(5) Takeuchi Y, Yamamoto T, Yonemaru J, Takemoto-Kuno Y, Fukuoka S, Kuroki M, Goto A, Matsubara K, Sato H, Hirabayashi H, Kobayashi N, Yamaguchi M, Ishii T, Ando I. Good eating quality QTLs, detected in two breeding populations by genome-wide association mapping, increase eating quality of an elite Japanese rice cultivar Koshihikari. Breed. Sci. 75: 358-368. doi.org/10.1270/jsbbs.25025 (2025. 12.)





